|
|
|
|
|
开发基于基序的深度学习酶挖掘策略,发现新型NADH依赖型亚胺还原酶 |
|
|
近日,华东理工大学郑高伟团队联合范贵生团队,开发出一种基于基序搜索的深度学习酶挖掘策略,成功挖掘出一类此前未被发现的天然NADH依赖型亚胺还原酶,为手性胺的高效生物合成提供了新酶催化剂与研究思路。2026年3月26日,相关成果已在线发表于Chem期刊,论文题目为“A motif-based deep learning tool for the identification of unusual NADH-dependent imine reductases”,共同第一作者为沈昕元博士生和吴宇轩博士生。
亚胺还原酶(IREDs)作为合成手性胺的重要生物催化剂,近年来已广泛应用于手性胺化学品的合成。然而,目前已报道的亚胺还原酶几乎均为NADPH依赖型,尚未见天然NADH依赖型亚胺还原酶的研究报道。
由于缺乏NADH依赖型亚胺还原酶的探针序列,传统依赖全序列比对的酶挖掘方法,无法实现对NADH依赖型亚胺还原酶的挖掘,成为制约新型亚胺还原酶发现的瓶颈。为突破这一难题,研究团队跳出传统全序列比对的思维框架,立足酶局部功能保守基序,开发出全新的PM2S(Protein Motif to Search)酶挖掘策略。
该策略整合了基序搜索、深度学习驱动的迭代检索与结果校准三大模块:首先参考结构同源酶的辅因子结合基序特征,设计出亚胺还原酶NADH结合的特异性基序,以此为基础对包含157,306条序列的3-羟基异丁酸脱氢酶家族数据库进行初筛,获得15个偏好NADH依赖性的种子蛋白。随后利用深度学习驱动的检索模块进行迭代扩大搜索范围,进而对候选酶进行辅因子类型校准,最终筛选得到95个候选的天然NADH依赖型亚胺还原酶。
经过聚类分析与实验验证,团队选取的代表性酶均表现出对NADH的显著辅因子偏好性,能高效利用NADH作为辅因子催化亚胺还原和还原胺化两类反应,且底物适应性广泛:可催化多种环状酮、脂肪族酮、醛类与不同位阻胺供体的偶联还原胺化反应,还能高效催化环状亚胺合成手性胺产物,对映选择性达99%以上。它们还能催化合成西那卡塞、替卡塞等药物的关键中间体,部分产物的制备效率优于传统NADPH依赖型酶,展现出良好的工业应用前景。
为揭示这类酶NADH偏好性的分子机制,该团队解析了酶-辅因子复合物结构,发现了辅因子结合口袋中的关键天冬氨酸(Asp)残基:该残基能与NADH形成稳定的空间和电荷相互作用,而NADPH的额外磷酸基团会因空间位阻和静电排斥难以结合。定点突变实验进一步证实,将该Asp残基突变为精氨酸(Arg)等带正电氨基酸后,酶的辅因子偏好性会彻底逆转,证实了该位点对辅因子选择性的决定性调控作用。
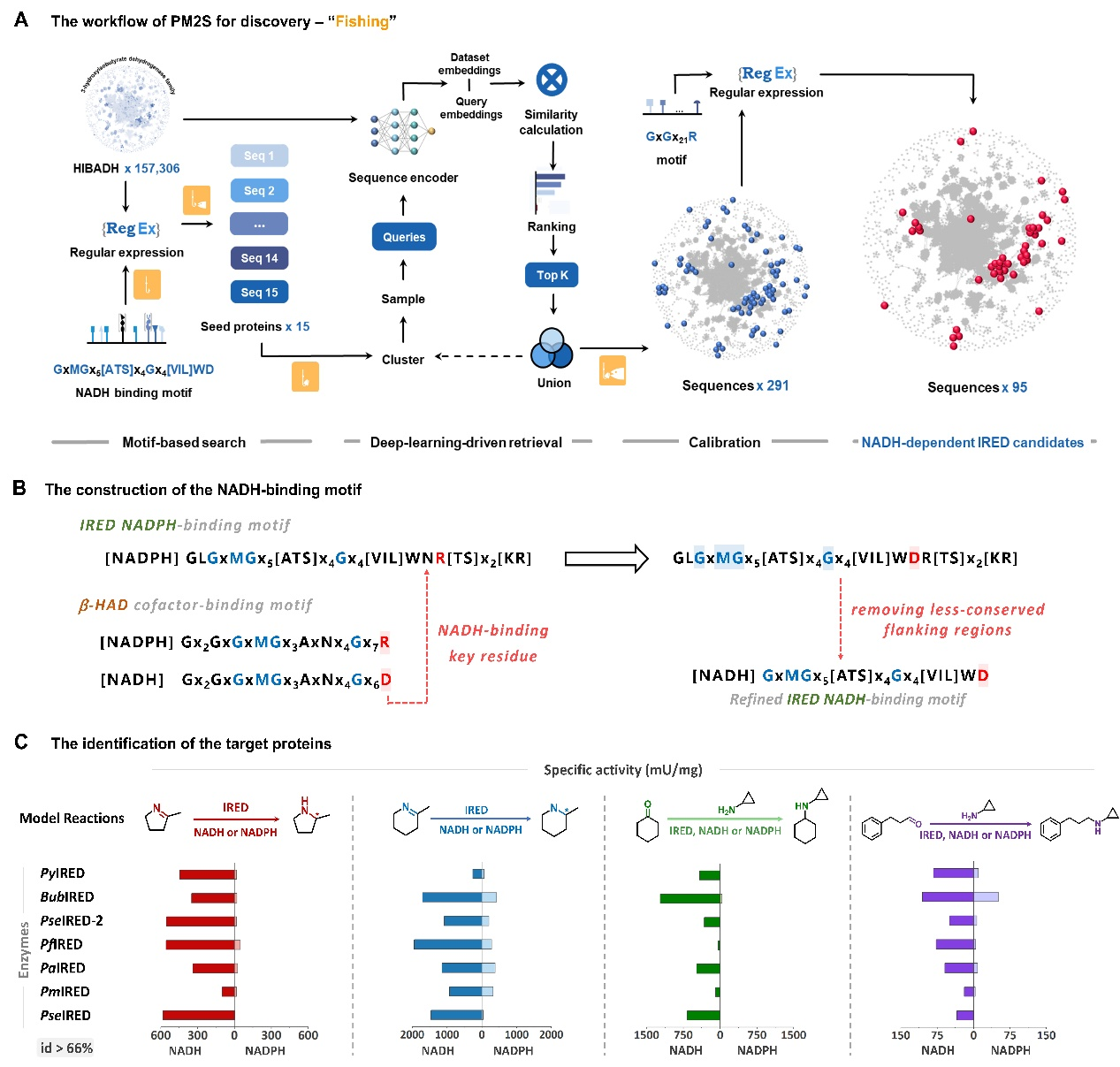
图1:基于PM2S方法挖掘潜在的NADH依赖型亚胺还原酶。
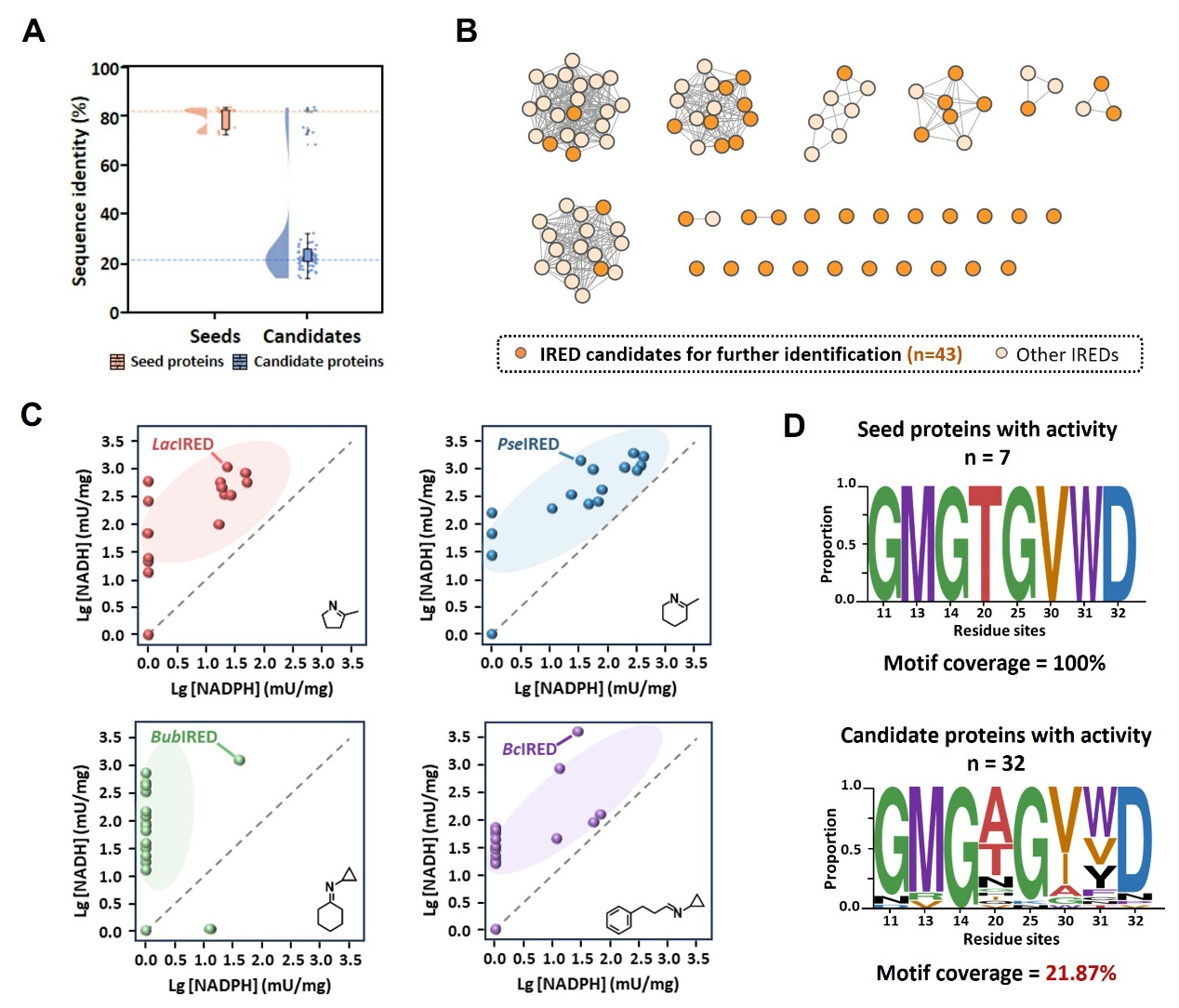
图2:通过PM2S方法挖掘到的NADH依赖型亚胺还原酶。
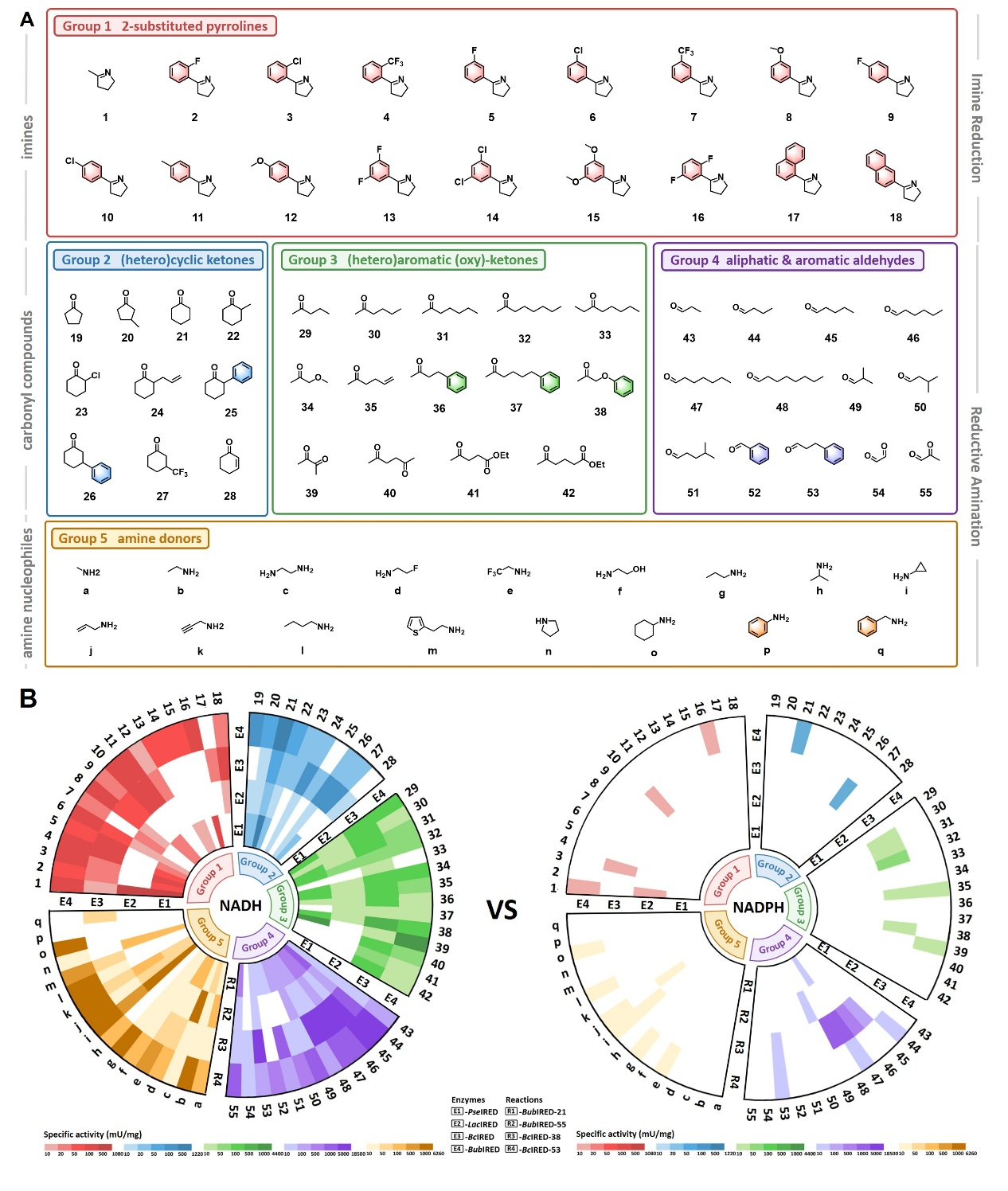
图3:NADH依赖的亚胺还原酶的底物谱。
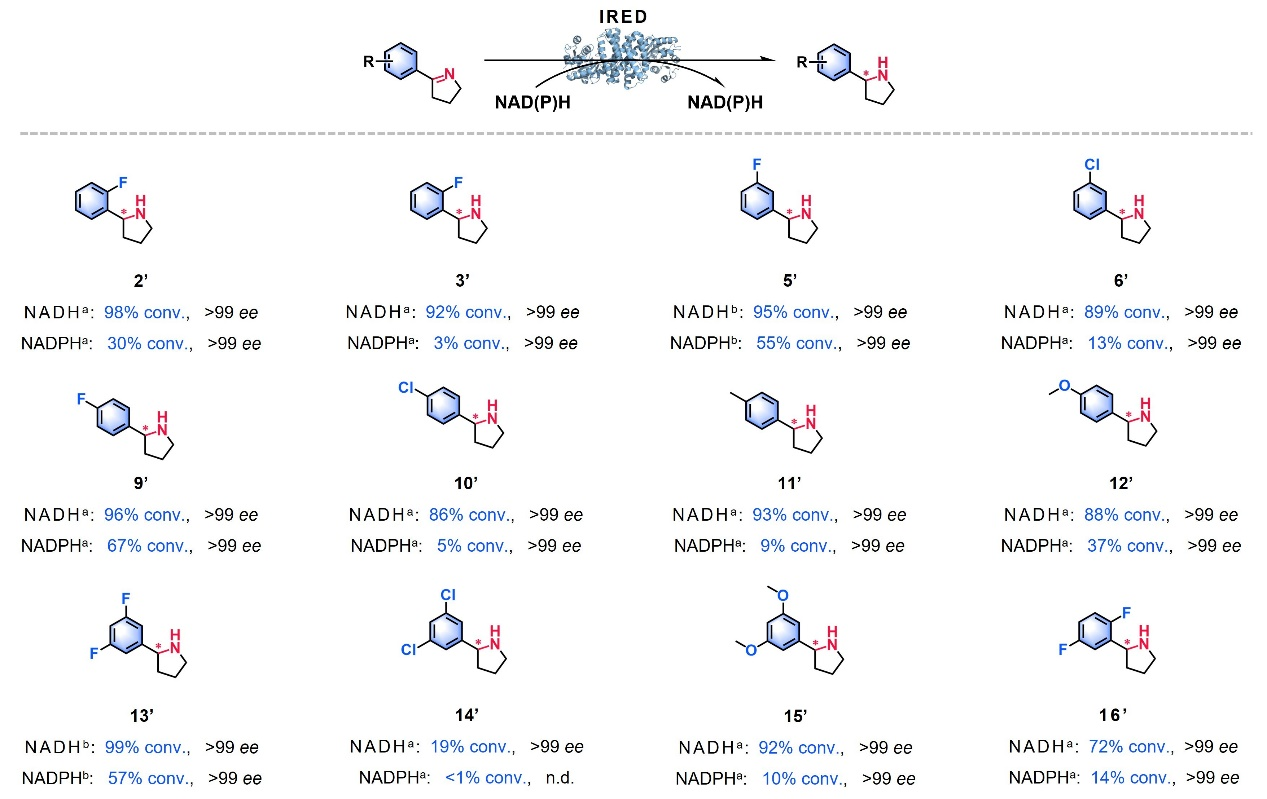
图4:NADH依赖的亚胺还原酶催化亚胺还原反应。
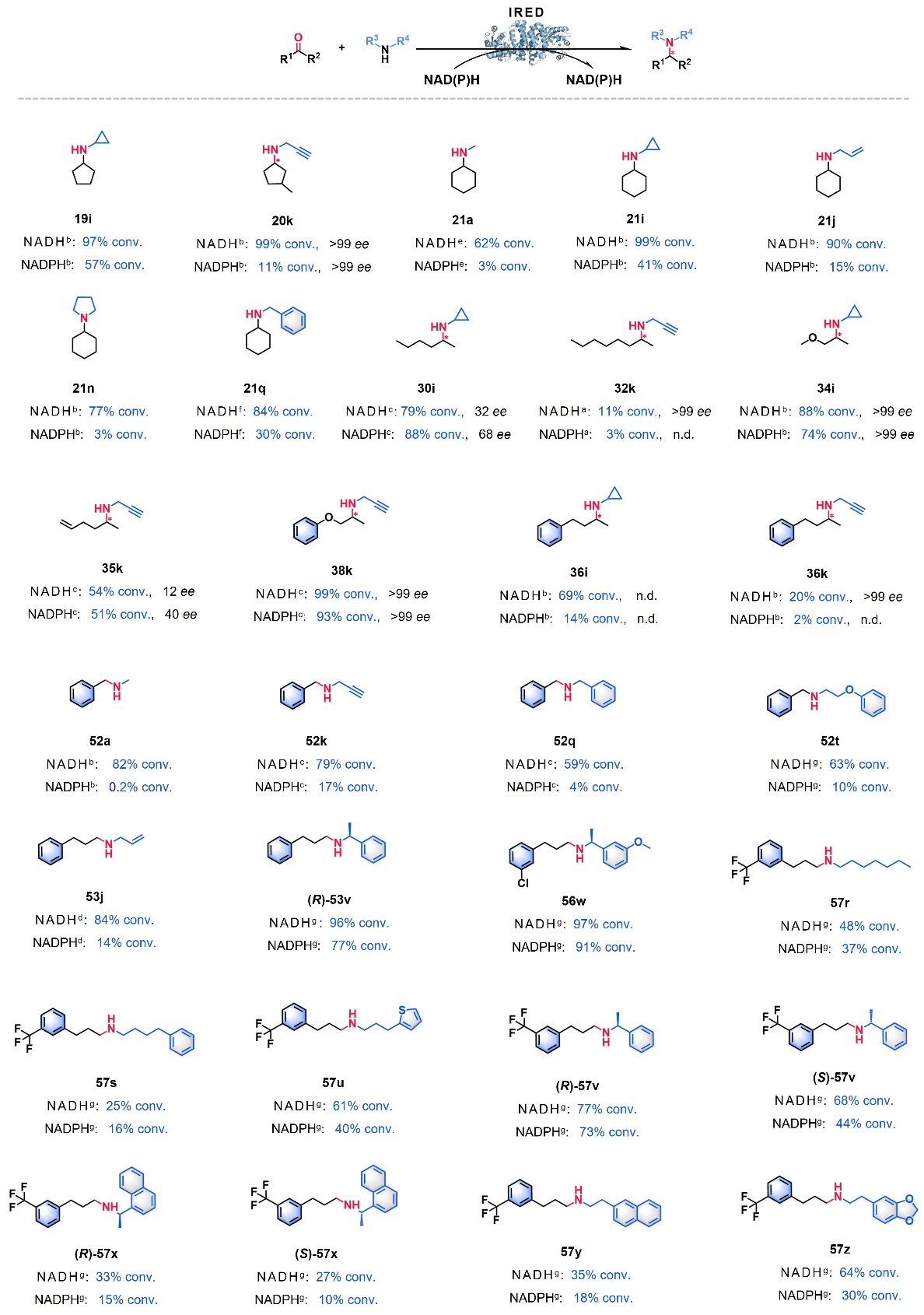
图5:NADH依赖的亚胺还原酶催化还原胺化反应。
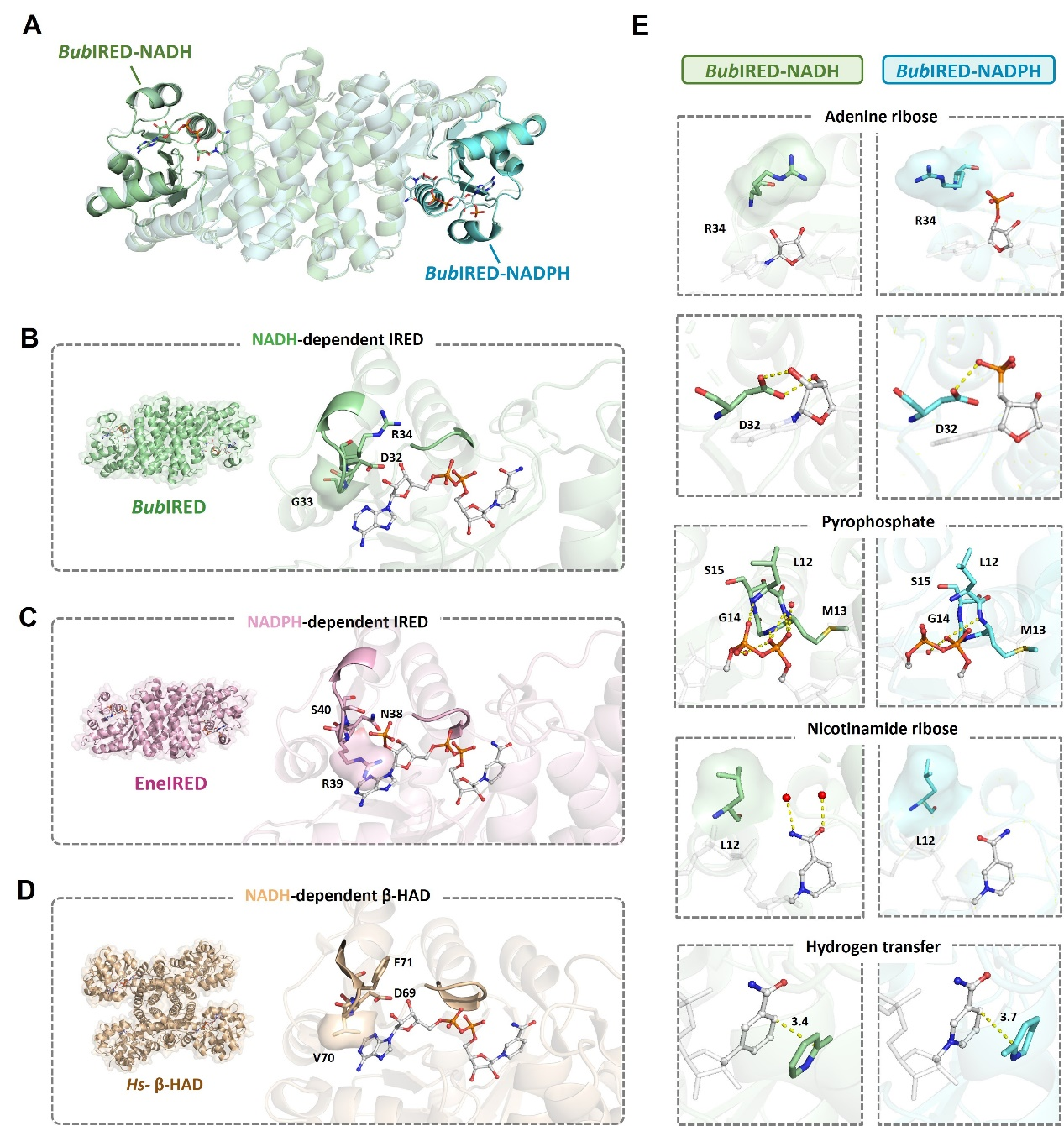
图6:酶-辅因子复合物结构分析。
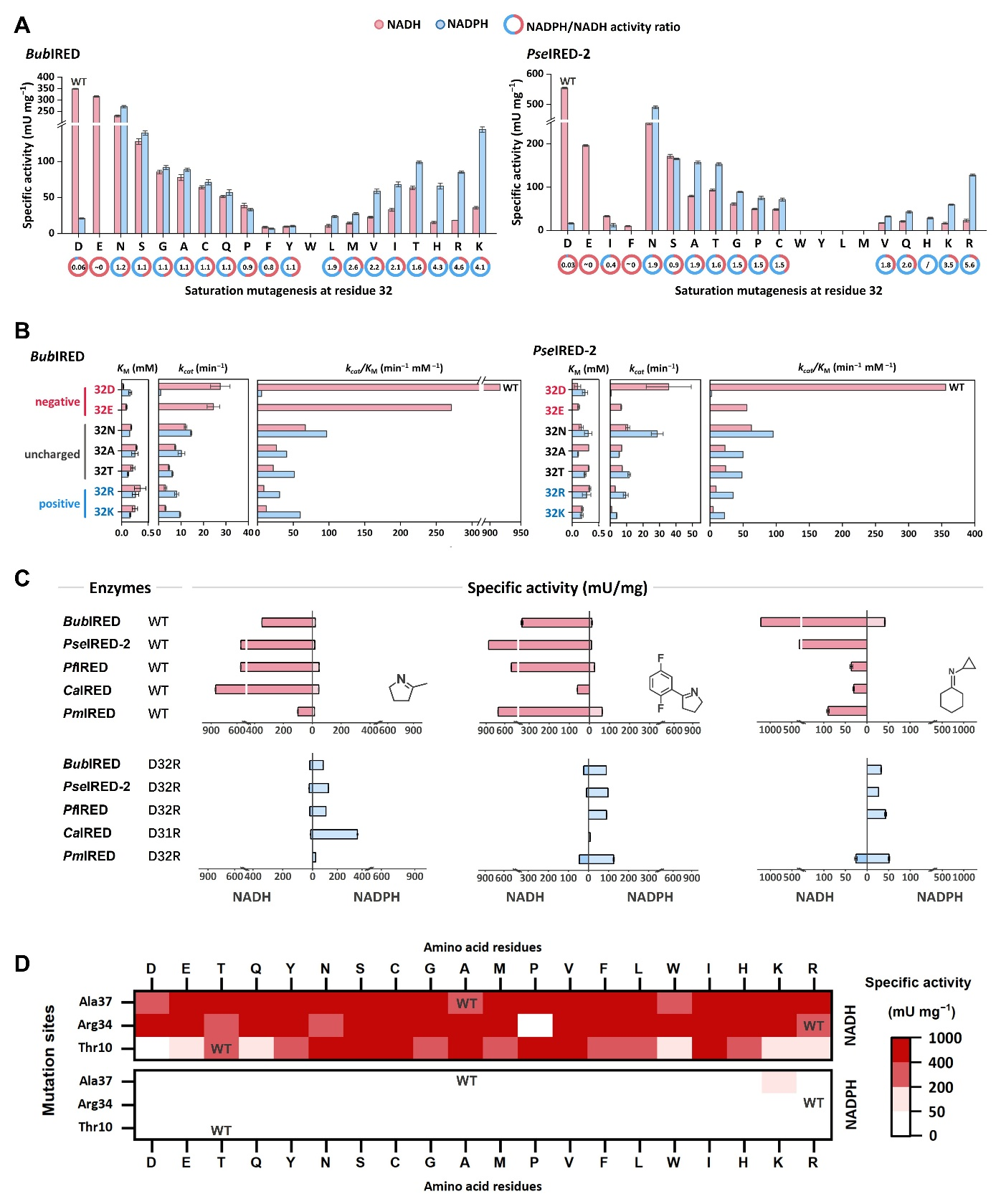
图7:NADH依赖型亚胺还原酶的关键残基突变实验。
综上,该研究构建了基于“局部保守基序 + 深度学习”的酶挖掘新范式,突破了传统方法的局限,为挖掘未被报道的功能酶家族提供了通用工具;发现了天然的NADH依赖型亚胺还原酶,丰富了IRED家族的多样性;阐明了辅因子选择性调控机制,为后续的酶工程改造及高效生物催化体系的构建奠定了基础。(来源:科学网)
相关论文信息:https://doi.org/10.1016/j.chempr.2026.102956