|
|
|
|
|
QB期刊 |多组学 + 代谢模型:系统生物学助力癌症分型与早诊迈向新高度 |
|
|
论文标题:Multi-omic data integration and exploiting metabolic models using systems biology approach increase precision in subtyping and early diagnosis of cancer
期刊:Quantitative Biology
作者:Ezgi Tanil, Emrah Nikerel
发表时间:28 Aug 2025
DOI:10.1002/qub2.70012
微信链接:点击此处阅读微信文章
癌症的早期诊断与精准分型一直是临床与科研中的难题。传统检测方法如活检具有侵入性,且难以重复进行;液体活检虽便捷,却受限于标志物发现难、数据异质性大、代谢组数据稀缺等挑战。
近期,Quantitative Biology期刊发表了一篇土耳其研究团队的论文,题目名为“ Multi‐omic data integration and exploiting metabolic models using systems biology approach increase precision in subtyping and early diagnosis of cancer”。文章提出了一种基于基因组尺度代谢模型的多组学整合框架,显著提升肺癌与胰腺癌的亚型分类与早期诊断精度。

全文概要
本研究提出了一种创新的系统生物学工作流程,通过整合多组学数据与基因组尺度代谢模型,显著提升了癌症亚型分类与早期诊断的精度。
研究团队首先将肺癌患者的转录组数据整合至人体基因组尺度代谢模型中,生成样本特异性的代谢流分布。随后,将这些代谢流数据与基因组、蛋白质组数据结合,构建多组学分类器。利用随机森林等机器学习方法及SHAP值分析,在肺癌中成功识别出与癌症状态、亚型及早期阶段相关的关键代谢通路(如脂质代谢、糖酵解)和生物标志物。该整合模型在区分癌组织与正常组织、肺癌亚型及早期阶段的任务中均表现出优异性能。此外,该流程在样本量有限的胰腺癌数据中同样验证有效,证明了其强大的稳健性与泛化能力。
本研究建立的方法框架不仅克服了代谢组数据稀缺的挑战,将基因型与表型动态关联,还为发现可操作的生物标志物和靶向通路提供了系统性工具。这项工作凸显了多组学整合与系统生物学建模在推动癌症精准诊断和个性化治疗方面的巨大潜力。
系统性研究框架
本研究构建了一套完整的多组学整合与系统生物学分析流程(图1):从基因组、转录组、蛋白质组与代谢流数据出发,通过基因组尺度代谢模型生成患者特异性代谢流分布,并利用机器学习进行高精度分类与标志物挖掘。
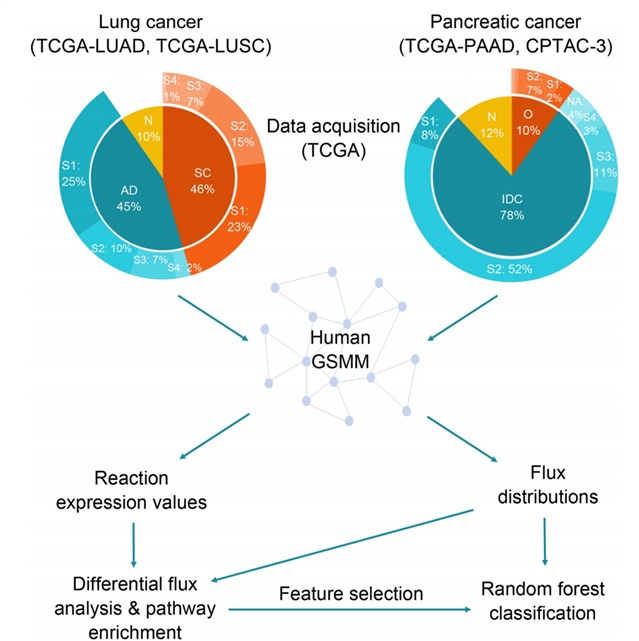
图1. 本研究采用的方法流程。
代谢流量建模 + 多组学整合,提升分类精度
通过将转录组数据导入人体代谢模型(Recon3D),生成患者特异性代谢流量分布,并结合基因组、蛋白质组数据,构建高精度多组学分类器。如图2所示, 在肺癌分类任务中,多组学整合模型(All)在癌 vs 正常(C/N) 和早期 vs 正常(S1/N) 分类中均达到接近完美的准确率(>95%),显著优于任何单一组学模型。该结果表明了整合不同数据层的必要性。
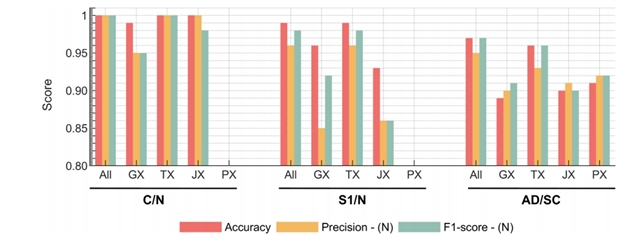
图2. 肺癌单组学分类器与整合多组学分类器性能对比
识别关键代谢通路与标志物,提供可解释性洞见
整合来自TCGA、NCBI-GEO、CCLE等多平台数据,利用随机森林与SHAP值分析,识别关键代谢通路与标志物。通路富集分析(图3)显示,在肺癌组织中,糖酵解、核苷酸代谢、脂质/脂肪酸代谢等通路显著激活,这些变化与癌症的“Warburg效应”及持续增殖等特征高度一致。
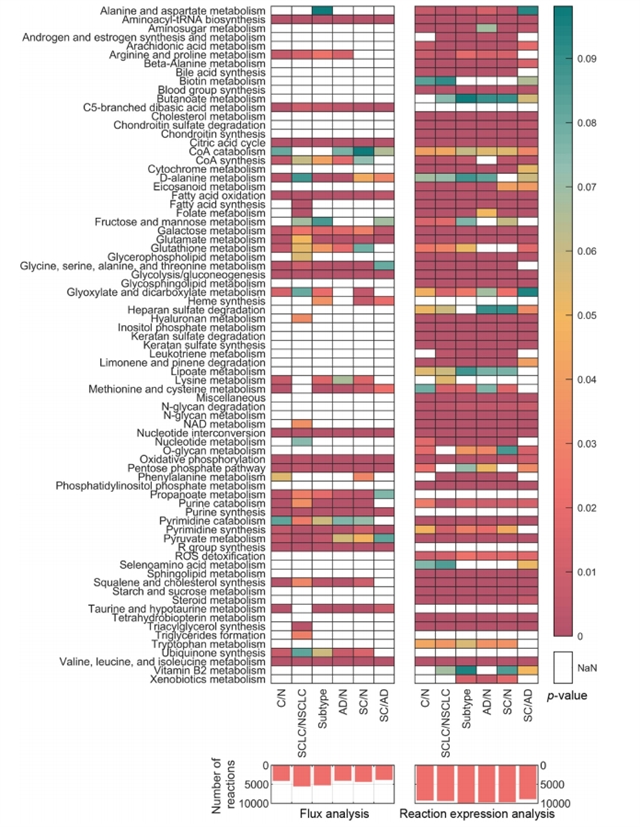
图3. TCGA数据集的通路富集分析
通过SHAP分析(图4),识别出各层面的关键标志物,例如:基因组层面上的THBS3、SEMA5A(调控细胞黏附与血管生成);代谢流层面上的G3PD1、SERPT(反映脂质与碳水化合物代谢重编程)。这些标志物为理解肺癌亚型差异和开发靶向疗法提供了新线索。
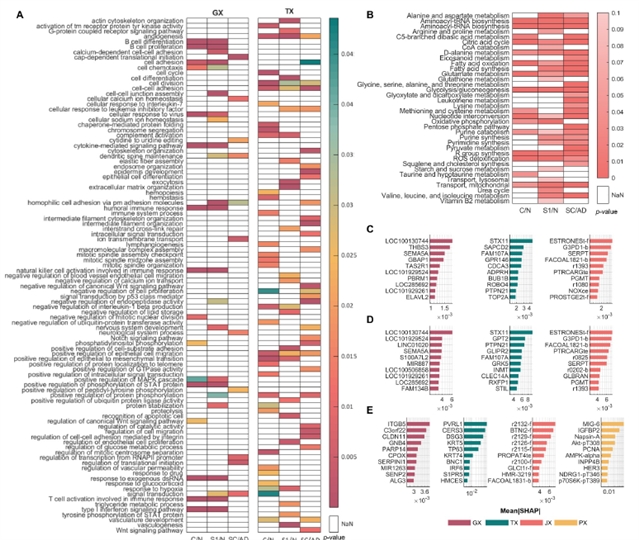
图4. 各单组学层中高重要性特征的功能分析(平均|SHAP|值 > 1e-4)
小样本稳健验证,展现强大泛化能力
即使在胰腺癌这类样本量稀缺的疾病中,该框架仍保持高分类精度,展示其强大的泛化能力与临床转化潜力。将同一流程应用于胰腺癌数据(图5),多组学整合模型再次展现出优异性能,证明了该方法在不同癌症类型中的稳健性与普适性。
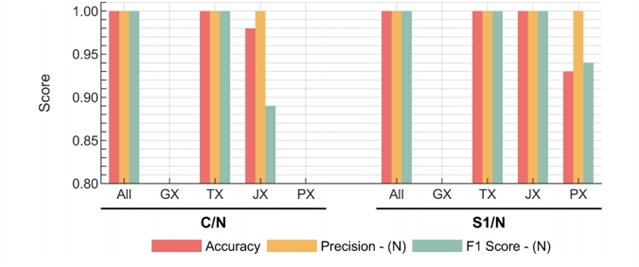
图5. 胰腺癌单组学分类器与整合多组学分类器性能对比
总结
该研究不仅为癌症代谢研究提供了新方法论,构建了一个从多组学数据到临床洞察的系统生物学桥梁,更为实现无创诊断、个性化治疗策略提供了可行路径。
QB期刊介绍
Quantitative Biology (QB)期刊是由清华大学、北京大学、高教出版社联合创办的全英文学术期刊。QB主要刊登生物信息学、计算生物学、系统生物学、理论生物学和合成生物学的最新研究成果和前沿进展,并为生命科学与计算机、数学、物理等交叉研究领域打造一个学术水平高、可读性强、具有全球影响力的交叉学科期刊品牌。
《前沿》系列英文学术期刊
由教育部主管、高等教育出版社主办的《前沿》(Frontiers)系列英文学术期刊,于2006年正式创刊,以网络版和印刷版向全球发行。系列期刊包括基础科学、生命科学、工程技术和人文社会科学四个主题,是我国覆盖学科最广泛的英文学术期刊群,其中12种被SCI收录,其他也被A&HCI、Ei、MEDLINE或相应学科国际权威检索系统收录,具有一定的国际学术影响力。系列期刊采用在线优先出版方式,保证文章以最快速度发表。
中国学术前沿期刊网
http://journal.hep.com.cn

特别声明:本文转载仅仅是出于传播信息的需要,并不意味着代表本网站观点或证实其内容的真实性;如其他媒体、网站或个人从本网站转载使用,须保留本网站注明的“来源”,并自负版权等法律责任;作者如果不希望被转载或者联系转载稿费等事宜,请与我们接洽。